罕见病基因组学
终结罕见病患者的诊断煎熬
通过医药健康领域的技术创新与合作让患者尽早获得诊断
罕见病基因组学与精准医学
理解罕见病的基因组学可以帮助医生精准定位未确诊疾病的病因,帮助患者家庭避免多年的医院就诊和不必要的检查。目前已知的罕见病超过7,000种1,且每年还有更多新发现。总体而言,2-6%的人口(>1.5亿人)受到罕见病影响1–3
罕见病诊断的漫长搜寻——"诊断之旅"——平均需要5至7年4,涉及多达8位医生5,以及2至3次误诊5。鉴于80%的罕见病是遗传性的或具有遗传成分6,全面的基因组测序增加了揭示患者潜在病因的可能性。新一代测序(NGS)为罕见病诊断提供了最高的可能性7-8,也是终结诊断之旅的最快途径7。
基因组学在罕见病诊断中的作用
基因组学正在推动罕见病诊断的根本转变,从症状分析到分子病因学评估。 了解疾病的生物学基础有助于实现更好的护理、更有针对性的治疗以及可预测的循证结果。 这种罕见病基因组学分子诊断是精准医疗的基础。
罕见病的分子诊断是至关重要的一步,它可以让患者、患者家庭、医生以及其他医护人员受益。美国医学遗传学与基因组学学会(ACMG)认为,确定患者的遗传病因对患者、患者家庭和整个社会都有很大的帮助。9
罕见病基因组学的优势
量身定制的疾病管理
对罕见病机制的了解能让医生将患者转诊给合适的专家,选择定制的疗法,并提供针对疾病的随访。
降低费用
罕见病的基因组诊断有助于避免冗长的诊断过程,尽量减少昂贵的检测和程序以及不必要的转诊。
生育咨询
确定罕见病的遗传模式可让患者、其直系亲属以及其他家庭成员了解复发风险,从而采取明智的计划生育。
社会心理学效益
除了避免诊断过程的相关压力外,接受分子诊断还可以将受影响的家庭聚集在罕见病支持团体的社区中。
社会效益
了解罕见病的基因组学机制有助于确定新的药物靶点并提高护理效率。
罕见病患者案例

结束Carson和Chase长达6年的诊断煎熬
Carson最初被诊断为患有脑瘫,但他的兄弟Chase证明了这是误诊。 四年后,全基因组测序诊断出Carson和Chase患有与线粒体烯酰辅酶A还原酶蛋白相关的神经变性(mitochondrial enoyl CoA reductase protein-associated neurodegeneration, MEPAN)。

Donovan的诊断历程
Donovan的症状与近十二种医学特征相吻合,引起了人们对20多种不同疾病的怀疑。 6年后,全基因组测序在SKI基因中发现了一个变异,而Donovan被诊断出患有Shprintzen-Goldberg综合征。

罕见病的基因组学诊断方法
罕见病的全基因组测序
全基因组测序是非常全面的罕见病检测方法。 它会检测整个基因组,并且能评估基因组编码区和非编码区中的变异。12-19
罕见病的全外显子组测序
全外显子组测序可评估外显子(基因组的编码区)中与疾病相关的变异。9,10,20
罕见病的靶向测序
靶向测序可分析与罕见病或罕见病家族相关的特定基因。
染色体芯片
染色体芯片(CMA)技术可识别整个基因组中较大的染色体变异和特定的已知变异。
比较罕见病的基因组学诊断方法
诊断率是常用的比较罕见病基因组检测方法的统计数据。 它是指检测提供进行分子诊断所需信息的可能性。 检测效能可能会因研究的患者人群和纳入标准的不同而有很大的差异。
全基因组测序
在大多数研究中,全基因组测序(WGS)在所有方法中展示了最高的检测效能。 它的基因组覆盖范围广(>97%),并且能够检测多种变异类型,包括单核苷酸位点变异、插入缺失、结构变异、拷贝数变异、重复延长、线粒体变异和旁系同源。10-17
全外显子组测序
全外显子组测序(WES)的检测力排第二。 与WGS相比,WES的基因组覆盖范围较小(覆盖了约1.5%的基因组),且检测到的变异类型较少。 但是,WES的价格比WGS便宜,并且其保险报销率通常更高。7–8, 18
靶向测序
罕见病的靶向测序可评估特定基因。 但最大的panel也只能覆盖不到0.5%的基因组。
染色体芯片
染色体芯片方法覆盖的基因组不到0.01%。 CMA主要关注包含经过充分鉴定的致病变异的基因组区域。 与WES和WGS相比,CMA的检测力要低得多。7

在线课程: 罕见病的临床测序
本课程简要介绍了儿童罕见病、可用的测试选项以及基因组测序的临床实施。该课程也许能为实验室供应商、医疗保健人员、医疗保健组织以及对其他对罕见病人群基因组学感兴趣的人提供相关信息。该课程获得了Illumina的教育资助。
查看课程详情
特色罕见病基因组学新闻

iHope项目扩大了使用范围
为受遗传病影响的家庭增加公平和改善结果的全球倡议

熊宝宝项目结果
该试点计划通过快速查明罕见病病因,为重症监护婴儿提供服务,它给婴儿及其家庭带来了希望。
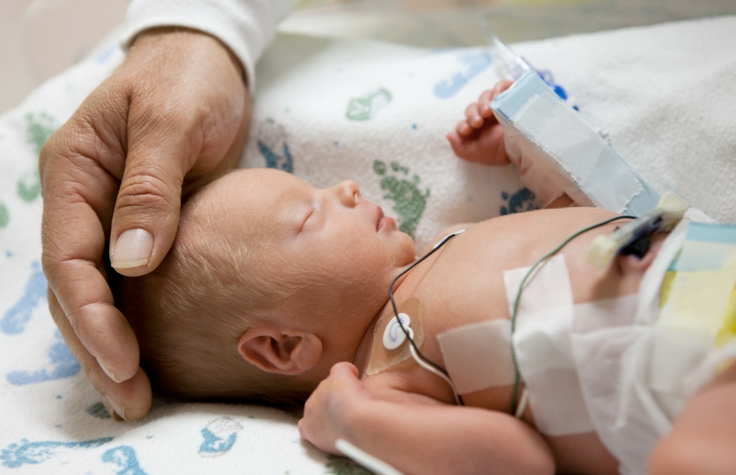
疑似患有罕见病的新生儿临床试验
NICUSeq是一项多中心研究,其目的评估全基因组测序是否可以改善急性病新生儿的临床护理。
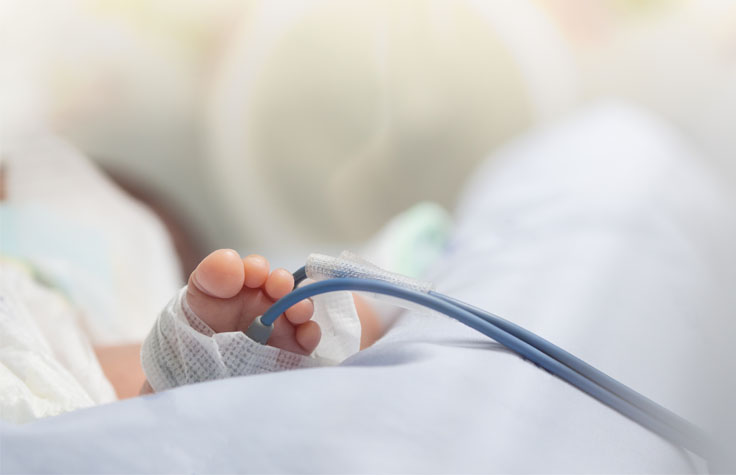
精准基因组学对罕见病的影响
逃离地狱
在这期播客节目中,来自澳大利亚未确诊遗传病组织(Syndromes Without A Name, SWAN)的Heather Renton介绍了女儿的罕见病、其诊断过程以及NGS的作用。
NICUSeq信息图
下载此信息图,了解全基因组测序对疑似遗传性疾病急性患病新生儿临床管理的影响。
一位母亲对诊断的追寻
树宝在很小的时候就患有肌张力亢进。全基因组测序在他的两个PDHX基因拷贝中分别发现了一个变异,从而为其实现了个性化的定制疗法。他的病情几乎立刻得到了改善。
参考文献
- Nguengang Wakap, S., Lambert, D.M., Olry, A. et al. Estimating cumulative point prevalence of rare diseases: analysis of the Orphanet database. Eur J Hum Genet. 2020;28:165–173. https://doi.org/10.1038/s41431-019-0508-0
- Ferreira CR. The burden of rare diseases. Am J Med Genet A. 2019;179(6):885-892. doi:10.1002/ajmg.a.61124
- Walker CE, Mahede T, Davis G, et al. The collective impact of rare diseases in Western Australia: an estimate using a population-based cohort. Genet Med. 2017;19(5):546-552. doi:10.1038/gim.2016.143
- Global Commission to End the Diagnostic Odyssey for Children with a Rare Disease. 2019.
- Rare Disease Impact Report: Insights from patients and the medical community. globalgenes.org/wp-content/uploads/2013/04/ShireReport-1.pdf.
- Bick D, Jones M, Taylor SL, Taft RJ, Belmont J. Case for genome sequencing in infants and children with rare, undiagnosed or genetic diseases. J Med Genet. 2019;56(12):783-791. doi:10.1136/jmedgenet-2019-106111.
- Clark MM, Stark Z, Farnaes L, et al. Meta-analysis of the diagnostic and clinical utility of genome and exome sequencing and chromosomal microarray in children with suspected genetic diseases. NPJ Genom Med. 2018;3:16. https://doi.org/10.1038/s41525-018-0053-8
- Vissers LE, Gilissen C, Veltman JA. Genetic studies in intellectual disability and related disorders. Nat Rev Genet. 2016;17(1):9-18. doi:10.1038/nrg3999
- ACMG Board of Directors. Clinical utility of genetic and genomic services: a position statement of the American College of Medical Genetics and Genomics. Genet Med. 2015;17(6):505-507. doi:10.1038/gim.2015.41
- Lionel AC, Costain G, Monfared N, et al. Improved diagnostic yield compared with targeted gene sequencing panels suggests a role for whole-genome sequencing as a first-tier genetic test. Genet Med. 2018;20(4):435-443. doi:10.1038/gim.2017.119
- Sanghvi RV, Buhay CJ, Powell BC, et al. Characterizing reduced coverage regions through comparison of exome and genome sequencing data across 10 centers. Genet Med. 2018;20(8):855-866. doi:10.1038/gim.2017.192
- Dolzhenko E, van Vugt JJ, Shaw RJ, Bekritsky, et al. Detection of long repeat expansions from PCR-free whole-genome sequence data. Genome Res. 2017;27(11): 1895-1903. doi: 10.1101/gr.225672.117.
- Gross, A.M., Ajay, S.S., Rajan, V. et al. Copy-number variants in clinical genome sequencing: deployment and interpretation for rare and undiagnosed disease. Genet Med. 2019;21:1121–1130. https://doi.org/10.1038/s41436-018-0295-y
- Alfares A, Aloraini T, Subaie LA, et al. Whole-genome sequencing offers additional but limited clinical utility compared with reanalysis of whole-exome sequencing. Genet Med. 2018;20(11):1328-1333. doi:10.1038/gim.2018.41
- Lindstrand A, Eisfeldt J, Pettersson M, et al. From cytogenetics to cytogenomics: whole-genome sequencing as a first-line test comprehensively captures the diverse spectrum of disease-causing genetic variation underlying intellectual disability. Genome Med. 2019;11(1):68. Published 2019 Nov 7. doi:10.1186/s13073-019-0675-1
- Chen X, Sanchis-Juan A, French CE, et al. Spinal muscular atrophy diagnosis and carrier screening from genome sequencing data. Genet Med. 2020;22(5):945-953. doi:10.1038/s41436-020-0754-0
- Chen X, Schulz-Trieglaff O, Shaw R, et al. Manta: rapid detection of structural variants and indels for germline and cancer sequencing applications. Bioinformatics. 2016;32(8):1220-1222. doi:10.1093/bioinformatics/btv710
- Srivastava S, Love-Nichols JA, Dies KA, et al. Meta-analysis and multidisciplinary consensus statement: exome sequencing is a first-tier clinical diagnostic test for individuals with neurodevelopmental disorders. Genet Med. 2019;21(11):2413-2421. doi:10.1038/s41436-019-0554-6